Covid-19 肺部 X 射线分类和 CT 检测演示(HealthShare 临床查看器与第三方AI PACS viewer整合)
Covid-19 肺部 X 射线分类和 CT 检测演示 关键字:COVID-19,医学影像,深度学习,PACS Viewer 和 HealthShare。
目的
在这场史无前例的新冠疫情笼罩之下, 我们竭尽所能为客户提供支援,同时利用先进的 AI 技术观察着不同的疫情战线。
去年,我简单提及了一个深度学习演示环境。 在这个漫长的复活节周末,我们就来看一看现实世界的图像,在 Covid-19 肺部 X 射线数据集上测试运行一些深度学习模型以进行快速分类,并见证这类用于 X 射线甚至 CT 的工具如何通过 docker 等方式快速部署到云端,实现及时的“AI 分诊”并协助放射科医生。
这只是一个 10 分钟的快速笔记,希望通过简单的方法帮助各位上手实践。
范围
本演示环境中使用了以下组件, 这是我目前能找到的最简单的形式:
- 一个小型匿名开放数据集,共 3 种类型:Covid-19 肺与细菌性肺炎肺与正常透明肺。
- 一组深度学习模型,如用于肺部 X 射线分类的 Inception V3 模型
- 带有 Jupyter Notebook 的 Tensorflow 1.13.2 容器
- 用于 GPU 工具的 Nvidia-Docker2 容器
- 配备 Nvidia T4 GPU 的 AWS Ubuntu 16.04 VM(如果不重新训练预训练的模型,笔记本电脑的 GPU 就足够了)
以及,
- “AI 辅助 CT 检测”的演示容器。
- 第三方 Open PACS Viewer 的演示容器。
- HealthShare Clinical Viewer 的演示实例。
以下不在演示范围内:
- PyTorch 越来越受欢迎(下次会用到)
- TensorFlow 2.0 在演示环境中的运行速度过慢(因此我暂时回转到 1.13 版)
- AutoML 等多模型集成(它们在现实世界中越来越流行,但单一老式模型对这个小数据集来说已经足够了)
- 任何现实世界位置的 X 射线和 CT 数据。
免责声明
这个演示更多是关于技术方法,而不是特定领域的临床试验。 基于 CT 与 X 线等证据的 Covid-19 检测已在网上广泛流传,对其有正面评价,也有负面评价。疫情期间,它在各个国家/地区和文化中发挥着不同的作用。 另外,本文的正文和布局可能会根据需要进行修改。 本文完全是出自“开发者”角度的个人观点。
数据
本测试的原始图像来自 Joseph Paul Cohen 公开的 Covid-19 肺部 X 射线集,以及开放的
Kaggle 胸部 X 射线集1>中的一些干净的肺,由 Adrian Yu 在 GradientCrescent 仓库1>中收集为一个小型测试集。 我在这里上传了测试数据,供有兴趣的读者进行快速测试。 到目前为止,它只包含一个小的训练集:
- 60x Covid-19 肺
- 70x 正常透明肺
- 70x 细菌性肺炎肺
测试
在以下测试中,我根据自己的情况做了些微调:
- Inception V3 模型作为基础,几个 CNN 层作为顶层
- 使用未冻结的底层 Inception 层权重进行迁移学习,以再训练(如果是在笔记本电脑 GPU 上,您只需要冻结预训练的 Inception 层)
- 为弥补目前收集到的少量数据集,略微增加了一些内容。
- 3x 类别而不是二元类别:Covid-19、正常与细菌性(或病毒性)肺炎(我将解释为什么是这三类)
- 计算基本的 3 类混淆矩阵,作为后续可能步骤的模板。
注:选择 InceptionV3 而不是其他流行的基于 CNN 的模型,比如 VGG16 或 ResNet50,并没有什么特别的原因。 我只是碰巧最近在其他模型中用它来演示运行了一个骨折数据集,为方便起见就直接重用了。 您可以使用任何偏好的模型重新运行以下 Jupyter Notebook 脚本。
我也在这篇帖子中附加了以下 Jupyter Notebook 文件。 下面也是为了快速说明。
1. 导入必要的库:
# import the necessary packages
from tensorflow.keras.layers import AveragePooling2D, Dropout, Flatten, Dense, Input
from tensorflow.keras.models import Model
from tensorflow.keras.optimizers import Adam
from tensorflow.keras.utils import to_categorical
from tensorflow.keras import optimizers, models, layers
from tensorflow.keras.applications.inception_v3 import InceptionV3
from tensorflow.keras.applications.resnet50 import ResNet50
from tensorflow.keras.preprocessing.image import ImageDataGenerator
from sklearn.preprocessing import LabelEncoder, OneHotEncoder
from sklearn.model_selection import train_test_split
from sklearn.metrics import classification_report, confusion_matrix
from imutils import paths
import matplotlib.pyplot as plt
import numpy as np
import cv2
import os2. 加载此处提供的示例图像文件
# set learning rate, epochs and batch size
INIT_LR = 1e-5 <span style="color:#999999;"># This value is specific to what model is chosen: Inception, VGG or ResNet etc.</span>
EPOCHS = 50
BS = 8
print("Loading images...")
imagePath = "./Covid_M/all/train" # change to your local path for the sample images
imagePaths = list(paths.list_images(imagePath))
data = []
labels = []
# read all X-Rays in the specified path, and resize them all to 256x256
for imagePath in imagePaths:
label = imagePath.split(os.path.sep)[-2]
image = cv2.imread(imagePath)
image = cv2.cvtColor(image, cv2.COLOR_BGR2RGB)
image = cv2.resize(image, (256, 256))
data.append(image)
labels.append(label)
#normalise pixel values to real numbers between 0.0 - 1.0
data = np.array(data) / 255.0
labels = np.array(labels)
# perform one-hot encoding for a multi-class labeling
label_encoder = LabelEncoder()
integer_encoded = label_encoder.fit_transform(labels)
labels = to_categorical(integer_encoded)
print("... ... ", len(data), "images loaded in multiple classes:")
print(label_encoder.classes_)Loading images... ... ... 200 images loaded in 3x classes: ['covid' 'normal' 'pneumonia_bac']
3. 添加基本数据增强,重新构建模型,然后开始训练
# split the data between train and validation.
(trainX, testX, trainY, testY) = train_test_split(data, labels, test_size=0.20, stratify=labels, random_state=42)
# add on a simple Augmentation. Note: too many Augumentation doesn't actually help in this case - I found during the test.
trainAug = ImageDataGenerator(rotation_range=15, fill_mode="nearest")
#Use the InveptionV3 model with Transfer Learning of pre-trained "ImageNet"'s weights.
#note: If you choose VGG16 or ResNet you may need to reset the initial learning rate at the top.
baseModel = InceptionV3(weights="imagenet", include_top=False, input_tensor=Input(shape=(256, 256, 3)))
#baseModel = VGG16(weights="imagenet", include_top=False, input_tensor=Input(shape=(256, 256, 3)))
#baseModel = ResNet50(weights="imagenet", include_top=False, input_tensor=Input(shape=(256, 256, 3)))
#Add on a couple of custom CNN layers on top of the Inception V3 model.
headModel = baseModel.output
headModel = AveragePooling2D(pool_size=(4, 4))(headModel)
headModel = Flatten(name="flatten")(headModel)
headModel = Dense(64, activation="relu")(headModel)
headModel = Dropout(0.5)(headModel)
headModel = Dense(3, activation="softmax")(headModel)
# Compose the final model
model = Model(inputs=baseModel.input, outputs=headModel)
# Unfreeze pre-trained Inception "ImageNet" weights for re-training since I got a Navidia T4 GPU to play with anyway
#for layer in baseModel.layers:
# layer.trainable = False
print("Compiling model...")
opt = Adam(lr=INIT_LR, decay=INIT_LR / EPOCHS)
model.compile(loss="categorical_crossentropy", optimizer=opt, metrics=["accuracy"])
# train the full model, since we unfroze the pre-trained weights above
print("Training the full stack model...")
H = model.fit_generator( trainAug.flow(trainX, trainY, batch_size=BS), steps_per_epoch=len(trainX) // BS,
validation_data=(testX, testY), validation_steps=len(testX) // BS, epochs=EPOCHS)... ... Compiling model... Training the full stack model... ... ... Use tf.cast instead. Epoch 1/50 40/40 [==============================] - 1s 33ms/sample - loss: 1.1898 - acc: 0.3000 20/20 [==============================] - 16s 800ms/step - loss: 1.1971 - acc: 0.3812 - val_loss: 1.1898 - val_acc: 0.3000 Epoch 2/50 40/40 [==============================] - 0s 6ms/sample - loss: 1.1483 - acc: 0.3750 20/20 [==============================] - 3s 143ms/step - loss: 1.0693 - acc: 0.4688 - val_loss: 1.1483 - val_acc: 0.3750 Epoch 3/50 ... ... ... ... Epoch 49/50 40/40 [==============================] - 0s 5ms/sample - loss: 0.1020 - acc: 0.9500 20/20 [==============================] - 3s 148ms/step - loss: 0.0680 - acc: 0.9875 - val_loss: 0.1020 - val_acc: 0.9500 Epoch 50/50 40/40 [==============================] - 0s 6ms/sample - loss: 0.0892 - acc: 0.9750 20/20 [==============================] - 3s 148ms/step - loss: 0.0751 - acc: 0.9812 - val_loss: 0.0892 - val_acc: 0.9750
4. 为验证结果绘制混淆矩阵:
print("Evaluating the trained model ...")
predIdxs = model.predict(testX, batch_size=BS)
predIdxs = np.argmax(predIdxs, axis=1)
print(classification_report(testY.argmax(axis=1), predIdxs, target_names=label_encoder.classes_))
<span style="color:#999999;"># calculate a basic confusion matrix</span>
cm = confusion_matrix(testY.argmax(axis=1), predIdxs)
total = sum(sum(cm))
acc = (cm[0, 0] + cm[1, 1] + cm[2, 2]) / total
sensitivity = cm[0, 0] / (cm[0, 0] + cm[0, 1] + cm[0, 2])
specificity = (cm[1, 1] + cm[1, 2] + cm[2, 1] + cm[2, 2]) / (cm[1, 0] + cm[1, 1] + cm[1, 2] + cm[2, 0] + cm[2, 1] + cm[2, 2])
<span style="color:#999999;"># show the confusion matrix, accuracy, sensitivity, and specificity</span>
print(cm)
print("acc: {:.4f}".format(acc))
print("sensitivity: {:.4f}".format(sensitivity))
print("specificity: {:.4f}".format(specificity))
<span style="color:#999999;"># plot the training loss and accuracy</span>
N = EPOCHS
plt.style.use("ggplot")
plt.figure()
plt.plot(np.arange(0, N), H.history["loss"], label="train_loss")
plt.plot(np.arange(0, N), H.history["val_loss"], label="val_loss")
plt.plot(np.arange(0, N), H.history["acc"], label="train_acc")
plt.plot(np.arange(0, N), H.history["val_acc"], label="val_acc")
plt.title("Training Loss and Accuracy on COVID-19 Dataset")
plt.xlabel("Epoch #")
plt.ylabel("Loss/Accuracy")
plt.legend(loc="lower left")
plt.savefig("./Covid19/s-class-plot.png")
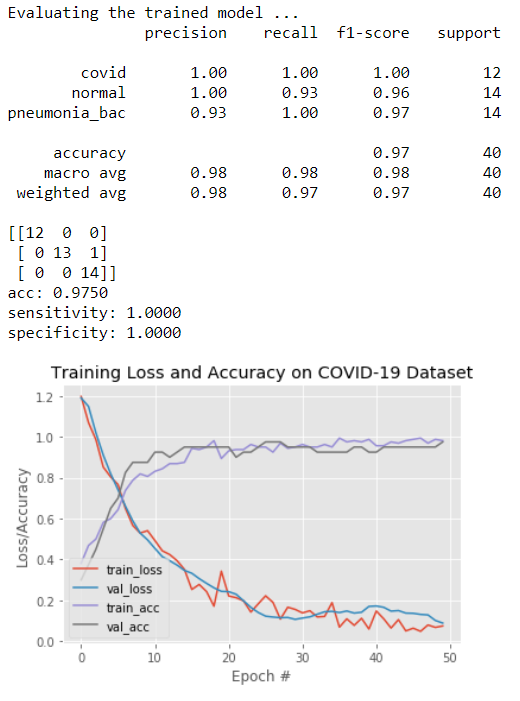
从上图可以看出,得益于“迁移学习”的好处,即使只有很小的数据集和不到 5 分钟的快速训练,得出的结果也并不差:12 个 Covid-19 肺全部正确分类,总共 40 个肺中只有 1 个正常肺被错划为“细菌性肺炎”肺。
5. 为测试真实 X 射线图绘制混淆矩阵
接下来,我们再深入一些,发送真实的 X 射线图测试这个轻度训练的分类器有多有效。
我将上述训练集或验证集中尚未使用的 27 个 X 射线图像上传到模型:
9 个 Covid-19 肺,9 个正常肺,9 个细菌性肺。 (图像也附在本篇帖子中。)
我只在第 2 步中修改了一行代码,确保它从不同路径加载测试图像:
...
imagePathTest = "./Covid_M/all/test"
...使用上面训练好的模型开始预测:
predTest = model.predict(dataTest, batch_size=BS) print(predTest) predClasses = predTest.argmax(axis=-1) print(predClasses) ...
最后,按照第 5 步重新计算混淆矩阵:
testX = dataTest testY = labelsTest ... ...
得出一些真实测试结果:
同样,经过训练的模型似乎能够正确分类所有 Covid-19 肺。 对于这么小的数据集来说,这样的结果不算太差。
6. 一些进一步的观察:
我在复活节周末尝试了许多种数据集,注意到从 AI 分类器的角度来看,Covid-19 肺似乎具有一些显著特征,相对更容易与其他正常细菌性或病毒性(流感)肺区分开来。
经过一些快速测试,我还发现,实在很难区分细菌性和病毒性(正常流感)肺。 如果有时间的话,我必须用 Ensemble 集群降低它们之间的差异,就像其他 Kaggle 竞争者在这种情况下可能会做的一样。
以上结果是否切实符合临床的真实情况? Covid-19 肺在 X 射线图上真有一些显著特征吗? 我并不确定。 这要向真正的胸部放射科医生征求意见。 就目前而言,我宁愿假设现在的数据集太小,还无法得出最终结论。
下一步:我很想收集更多的真实 X 射线图,用 xgsboot、AutoML 或新的 IRIS IntegratedML 工作台全面观察。 还有,我希望我们能够为临床医生和 A&E 分诊医生将 Covid-19 肺按其严重程度进一步分为如 1 级、2 级和 3 级。
不管怎样,我还是附上了数据集和 Jupyter Notebook。
部署
在这个“医学影像”领域,我们已经触及了一些快速设置的简易起点。 实际上,这个 Covid-19 领域是我在过去一年中用周末时间和长假研究的第 3 个领域。 其他包括“人工智能辅助骨骨折检测”系统和“人工智能辅助眼(眼科)视网膜诊断”系统。
上面的模型也许还太过简陋,但是我们可能很快就必须面对一个常见问题:我们要如何将其部署为一种“AI 服务”?
这涉及技术堆栈和服务生命周期,还涉及实际的“用例” - 我们要解决哪些问题?它可以提供什么样的实际价值? 答案有时并不像技术本身那样清晰。
英国 RCR (Royal College of Radiologist) 草案提出了 2 个简单的用例:“放射科医生的 AI 助手”和“A&E 或基层医疗环境中的 AI 分诊”。 我个人表示同意,并认为“AI 分诊”目前来说更有价值。 幸运的是,得益于云、Docker、AI 以及我们的 HealthShare 的支持,如今的开发者可以运用更多资源应对这类用例。
例如,以下屏幕截图显示了 AWS 托管的企业级“Covid-19 肺 AI 辅助 CT 检测”服务,及其如何直接嵌入 HealthShare Clinical Viewer 进行演示。 与 X 射线类似,DICOM 中的 CT 集可以直接上传或发送到这个打开的 PACS Viewer,点击“AI diagnosis”即可在 10 秒内根据训练的模型给出 Covid-19 概率的定量指示,能够全天候用于快速“AI 分诊”用例。 X 射线分类等模型可以在同一患者的相关信息中,以相同的方式在现有 PACS 查看器上部署和调用,帮助一线临床医生。
致谢
测试图像来自 Joseph Paul Cohen 的 Covid-19 肺部 X 射线集,以及开放的 Kaggle 胸部 X 射线集中的一些干净的肺,由 Adrian Yu 在 GradientCrescent 仓库中收集。 我还重用了 PyImageSearch 的 Adrian 的结构,添加了我自己改进的训练,如“测试”部分所列。 还要感谢 HYM 提供基于 AWS 云的 Open PACS Viewer 以及 X 射线和 CT 图像的 AI 模块,用于研究测试数据集。
未来计划
如今,AI 已经“侵入”到人类健康和日常生活的的方方面面。 根据我高度简化的观点,医疗领域的 AI 应用可能主要有以下几个方向:
- 医学影像:包括胸部、心脏、眼睛和大脑等的 X 射线、CT 或 MRI 等图像。
- NLP 理解:对海量文本资产和知识库的挖掘、理解和学习。
- 人口健康:包括流行病学等趋势预测、分析和建模。
- 个性化 AI:一组专为个人训练的 AI/ML/DL 模型,作为个人健康助手与用户一起成长和变老?
- 其他 AI:如 AlphaGo,甚至用于 3D 蛋白结构预测来对抗 Covid-19 的 AlphaFold 等,这些前沿突破让人印象深刻。
谁也无法预测我们将来能取得什么样的成果。 而且,这本来就是一个愿望清单,只要我们别在家里待得太久。
附录 - 文件已上传到此处。 其中包括上文使用的图像和提及的 Jupyter Notebook 文件。 在周末从头开始设置和运行可能要花费几个小时的时间。